近日,儿科罕见病教育部重点实验室夏昆研究员、李津臣研究员、夏露副研究员在Science Bulletin上发表了题为“Haplotype-Resolved Long-Read Sequencing Reveals Parent-of-Origin Effects of Tandem-Repeat Variation in Autism Spectrum Disorder”(基于长读长测序解析孤独症单倍型水平串联重复变异的亲本来源效应)的研究成果(doi.org/10.1016/j.scib.2026.03.058)。该研究基于长读长测序技术,在单倍型水平解析了串联重复序列(TandemRepeat,TR)变异与孤独症谱系障碍(Autism Spectrum Disorder, ASD)的相关性及其亲本来源效应,为深入理解ASD的遗传基础提供了新视角。

ASD是遗传度高达80%的复杂神经发育障碍,核心临床表现包括社交沟通障碍、狭隘兴趣和重复刻板行为。约10-20%的病例可由已知变异解释,但多数遗传风险仍未明确。TRs广泛分布于基因组中,但由于传统测序读长限制,既往研究仅关注短串联重复序列(STR)的异常扩增,未能系统评估STR收缩、可变数目串联重复序列(VNTR)异常变异及其亲本来源效应。
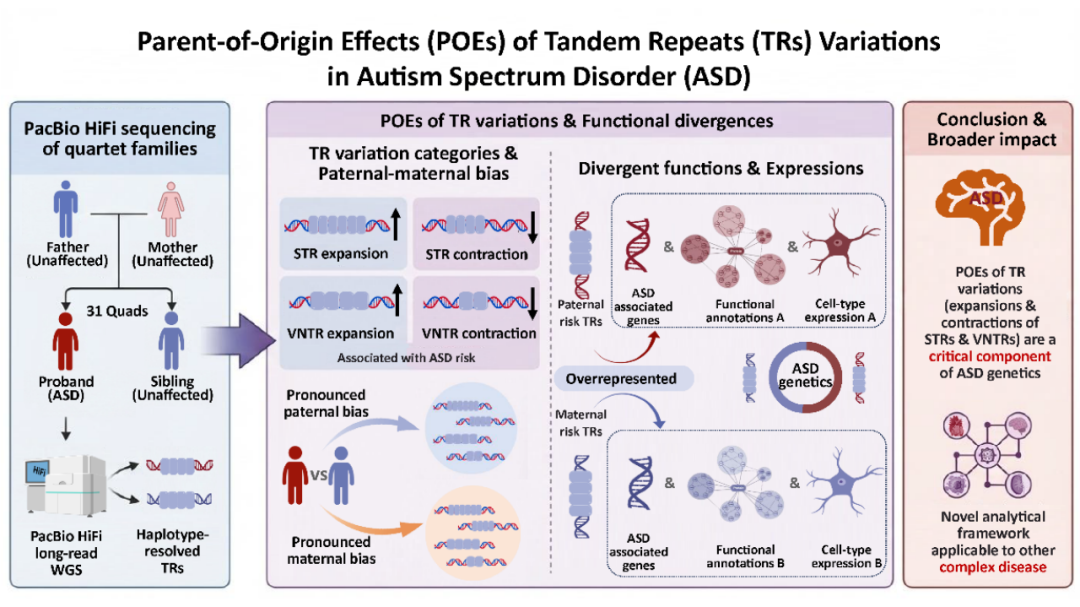
本研究基于中国孤独症临床与遗传资源队列(ACGC),对31个四人家系(共124个样本)进行全基因组PacBio HiFi长读长测序,在单倍型水平量化了超100万个STR和VNTR的重复次数。结果显示,ASD先证者中STR和VNTR的异常收缩与扩张均显著多于未患病同胞,且不同类别TR变异常表现出父本或母本偏好。尽管父本和母本来源的风险TR均富集于ASD相关基因,但二者在调控元件、功能通路及细胞特异性表达上呈现不同特征,提示不同亲本来源的TR可能通过不同机制影响ASD风险。
儿科罕见病教育部重点实验室夏昆研究员、李津臣研究员和夏露副研究员为该论文的共同通讯作者,李津臣研究员、罗腾飞博士和任雪博士为该论文共同第一作者。该项工作得到了国家自然科学基金重点项目、国家自然科学基金国际(地区)合作与交流项目、中国科协青年人才托举工程、湖南省重点工程项目、湖南省自然科学基金、以及芙蓉实验室科技攻关项目的支持。
夏昆/郭辉/李津臣/胡正茂/夏露团队长期致力于孤独症遗传基础研究,建成国内最大规模的孤独症临床遗传资源库(ACGC),主导国际合作,发现十余个神经发育疾病新基因,自主研发多项遗传分析工具与数据库,成果惠及全球107个国家、四千余家科研单位。近年来,团队利用三代测序技术拓展至非编码区复杂变异研究,系统揭示了中国人群孤独症从常见到罕见、从单核苷酸到结构变异的多维度遗传图谱。相关成果发表于 Science Bulletin、Science Advances、Nature Communications 等国际顶尖期刊。
儿科罕见病教育部重点实验室聚焦神经系统发育异常、代谢及线粒体相关重要儿科罕见病,建立临床队列,开展表型组、遗传与表观遗传学基础、分子发病机制、诊断与治疗新技术的基础和应用研究,建设儿科罕见病数据库与信息平台,开发新型诊疗技术,开展科普宣传与教育,培养高水平专门人才,提高我国儿科罕见病基础研究和诊疗水平,降低发病率,提升治疗效果。建成具有国际竞争力的儿科罕见病研究基地、临床诊疗中心和人才培养基地,服务健康中国战略。